article rédigé dans le cadre du ChallengeAZ 2020
J’ai voulu aller un cran plus loin dans l’exploration de mes origines génétiques, en effectuant une analyse spécifique du chromosome Y. Pour ce faire, j’ai effectué un test auprès du laboratoire Family Tree DNA. Voici les premiers résultats.
L’intérêt de faire un test du chromosome Y
Le chromosome Y est l’un des plus petits chromosomes. Il est transmis uniquement de père en fils, et sans recombinaison, de sorte qu’il permet de remonter à la fois la lignée généalogique et la lignée archéologique :
- l’intérêt généalogique
L’analyse du chromosome Y permet de retrouver tous les membres masculins issus de la même branche. Ainsi, un garçon aura le même chromosome Y que son père, son grand-père paternel ou son arrière-grand-père paternel, mais aussi que son oncle paternel, ses fils et ses cousins du côté paternel…
- l’intérêt archéologique
L’analyse du chromosome Y permet de connaître l’histoire de ses ancêtres patrilinéaires depuis la préhistoire, et de repérer sa branche dans « l’arbre génétique de l’humanité ».
Le test Big-Y de Family Tree DNA
J’avais déjà obtenu un tout premier niveau d’analyse du chromosome Y via le test de base de 23andMe, qui avait trouvé sur mon haplogroupe paternel R-FGC13326. Mais Family Tree DNA est le seul parmi les gros laboratoires du marché à proposer une gamme de tests spécifiques à l’analyse au chromosome Y.
Le test Big-Y est aujourd’hui le plus complet, mais aussi le plus cher car il examine 700 STR et plus de 200 000 SNP (essayez de le commander lors des nombreuses périodes d’offres promotionnelles)
- le test Y-SNP s’effectue sur les marqueurs SNP (single-nucleotide polymorphism). Ce sont des mutations quasiment uniques, c’est-à-dire qu’une personne a eu un jour cette mutation, et tous ceux qui l’ont aujourd’hui, en sont les descendants. On peut alors faire l’arbre génétique de l’humanité. Ce test est utilisé pour connaître l’histoire de ses ancêtres patrilinéaires depuis la préhistoire.
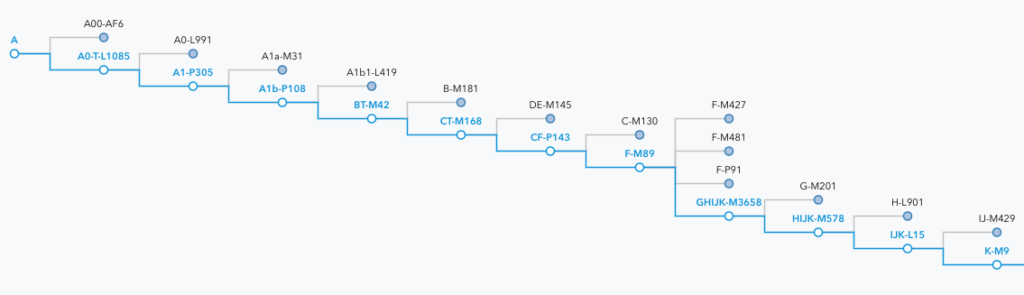
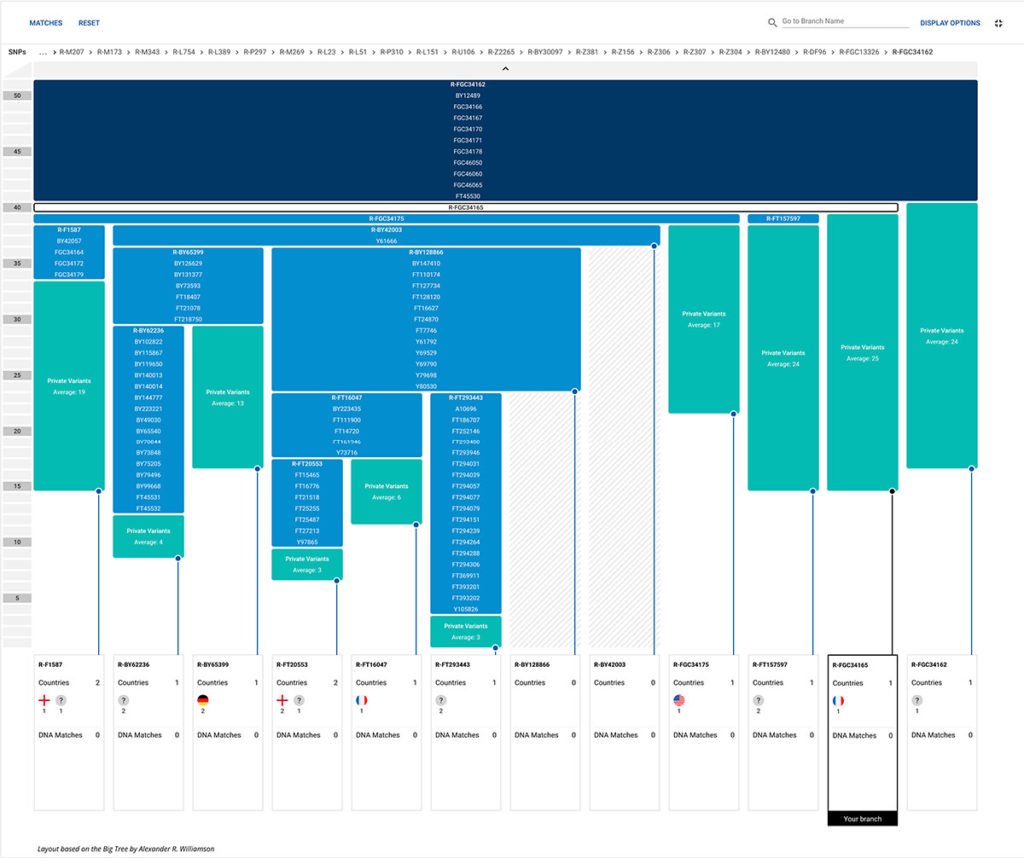
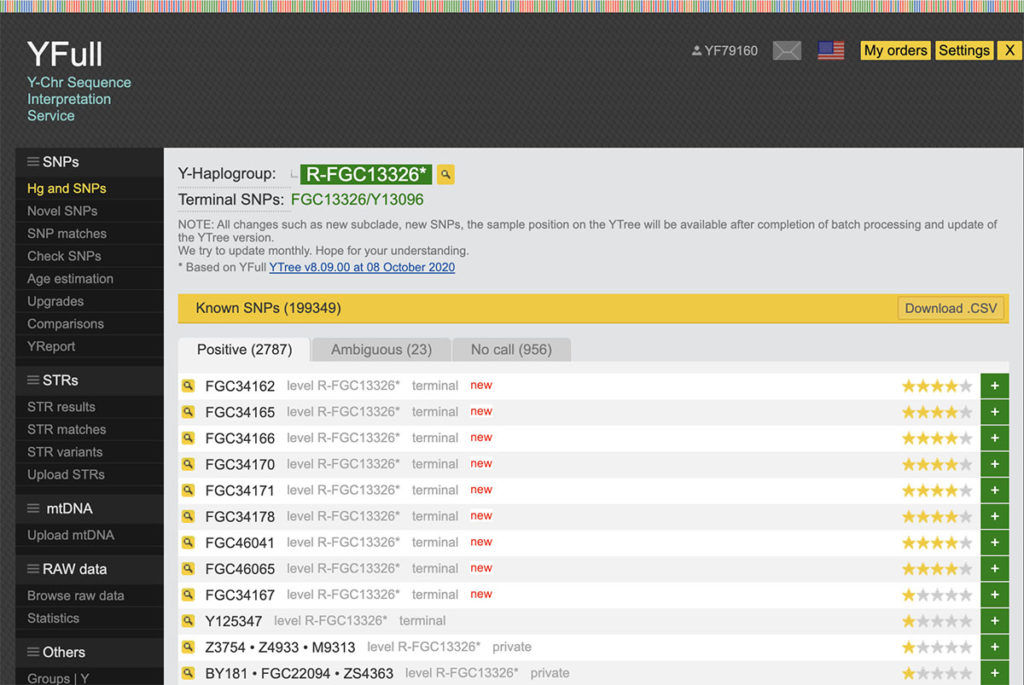
Mon SNP Terminal est R-FGC34165, c’est la branche la plus récente de l’haplogroupe dont je descends.

Et ce SNP est ensuite présenté par Family Tree DNA dans son haplotree avec l’ensemble des haplogroupes antérieurs qui ont également été testés positifs avec mon ADN.
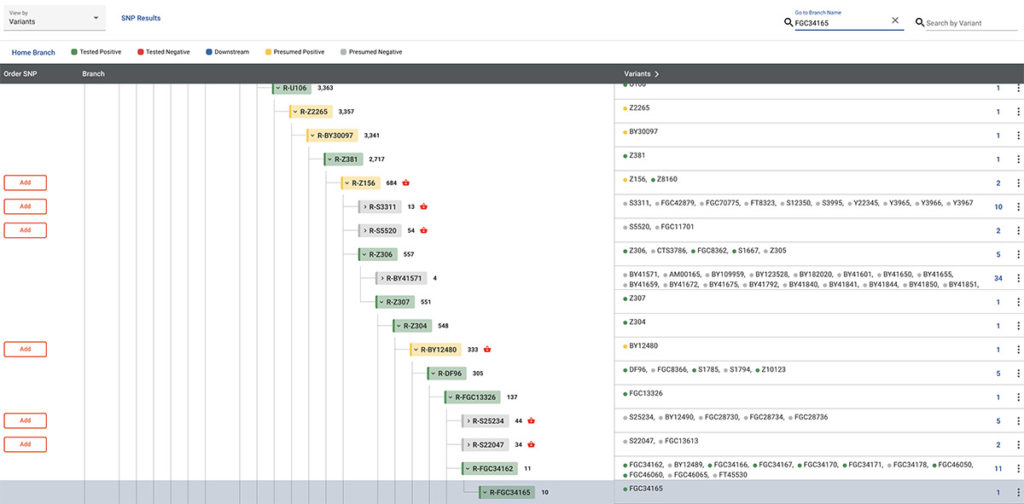
Enfin sur le Big-Y blocktree, je constate que Family Tree DNA a trouvé 25 SNP qui me sont propres, mais qui ne permettront d’avoir un haplogroupe plus récent uniquement quand j’aurai des matchs Big-Y.
- le test Y-STR s’effectue sur les marqueurs STR (short tandem repeat). On compte le nombre de séquences répétées sur un marqueur donné. Plus il y a de marqueurs ayant le même nombre des séquences répétées entre deux individus, plus il y a de chance qu’ils soient issus du même ancêtre patrilinéaire. Ce test est utilisé pour rechercher des cousins relativement proches à l’échelle de l’humanité (2 000 ans à aujourd’hui), par exemple sur un projet de nom de famille.
Un STR est désigné par un numéro DYS (DNA Y-chromosome Segment number). Voici comme se présente sur Family Tree DNA le résultats des test STR :
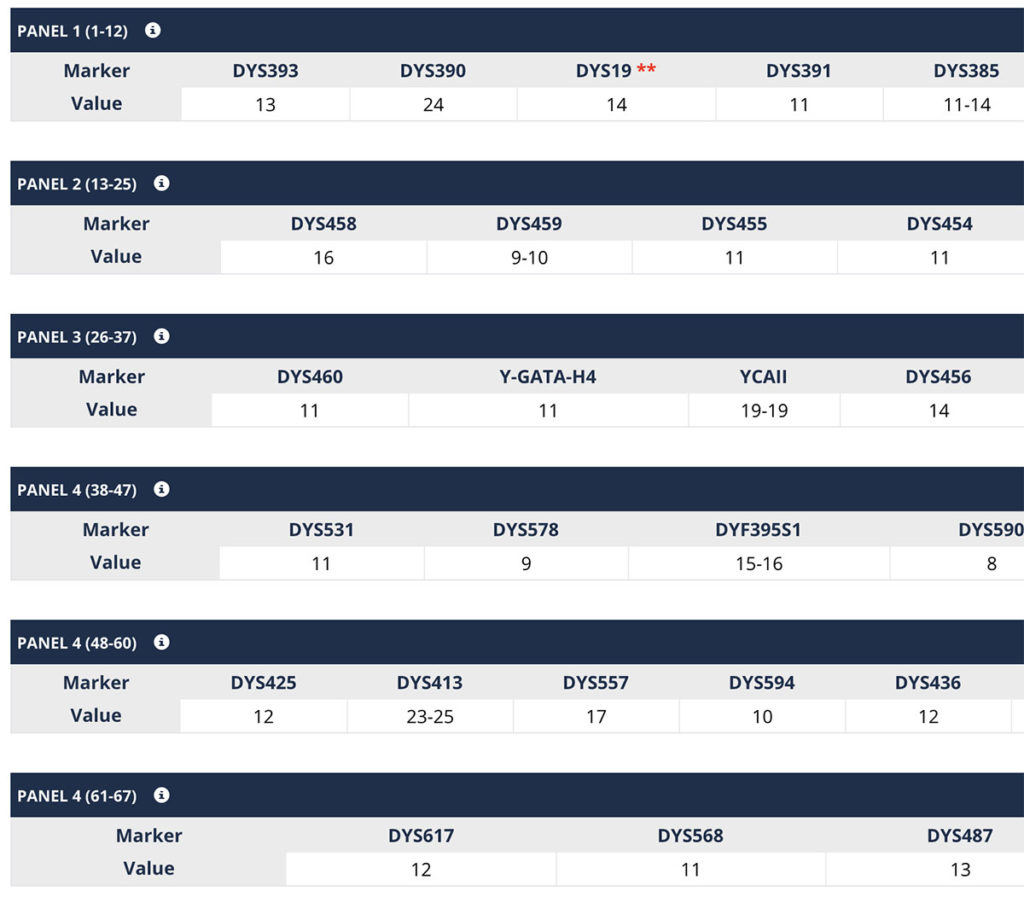
Ces résultats sont ensuite comparés à une liste de cousins génétiques potentiels, et permettent d’estimer le nombre de générations me séparant de ces cousins.
Les matchs Y sur Family Tree DNA
Alors, quelles sont les correspondances génétiques identifiées ? Pour l’instant elles sont rares et peu exploitables…
Je n’ai aucun match Big-Y, ni sur 111, 67 ou 37 marqueurs. Je n’ai que 13 matchs sur 25 marqueurs, et plus de 4 000 sur 12 marqueurs.
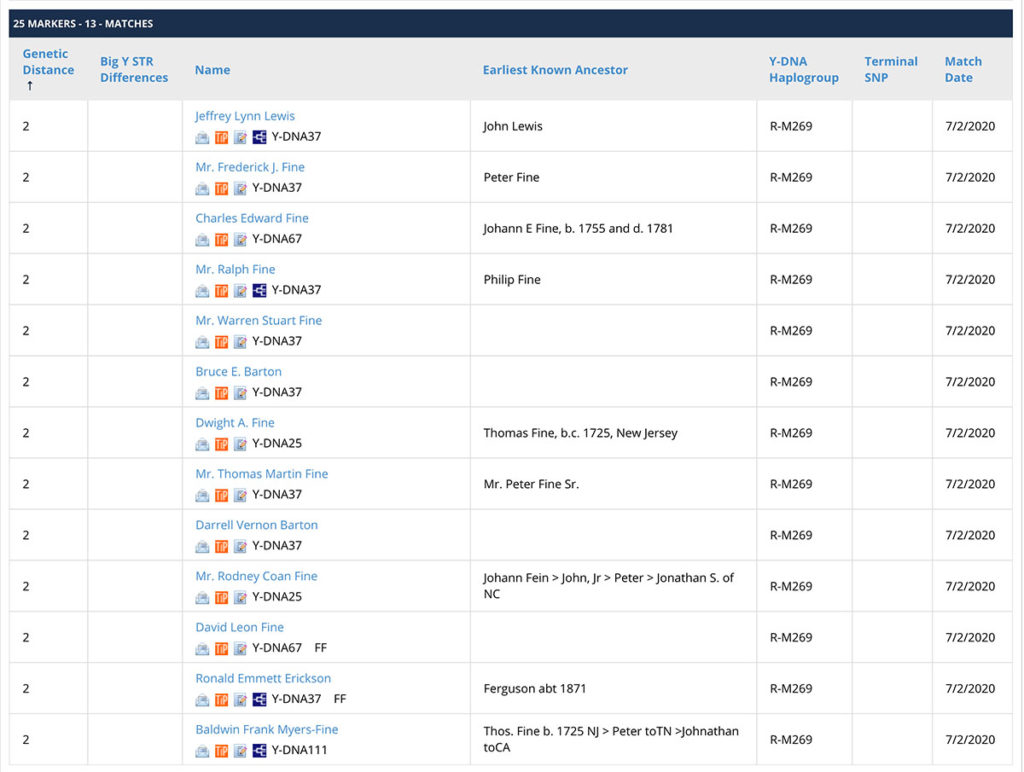
Sur 25 marqueurs, la distance génétique avec ces cousins est de minimum 2. Cela signifie que sur les 25 marqueurs analysés, il y a 2 mutations entre mes résultats et ceux de ces cousins (soit 1 mutation sur 2 des marqueurs, soit 2 mutations sur un des marqueurs). D’après le tableau Expected Relationships with Y-DNA STR Matches, nous avons probablement un ancêtre commun sur notre lignée paternelle, mais il doit se situer à la limite des données généalogiques (approximativement entre la 6ème et la 15ème génération).
Dès qu’un nouveau match Y arrive dans la base Family Tree DNA, je reçois un notification. Mais pour l’instant je n’ai pas de cousin qui soit suffisamment proche et qui aurait effectué un test ADN-Y (il faut dire que ce n’est pas encore très « grand public » en France, c’est plus cher qu’un test autosomal, et aucun site qui le propose n’est en français…).
Un service complémentaire : YFull
On m’a conseillé en parallèle de soumettre les données brutes sur le site YFull. Ce service recueille les fichiers ADN bruts de 11 laboratoires différents que les utilisateurs veulent bien leur soumettre. Ainsi, mon chromosome Y sera comparé à celui des utilisateurs de Family Tree DNA, mais aussi par exemple à ceux qui ont fait séquencer tout leur génome chez Dante Labs.
Il faut commencer par télécharger les données brutes à partir de Family Tree DNA, et cette opération est facturée 99$… Vous obtenez sous quelques heures votre fichier au format BAM qui pèse plus de 400 Mo, et également un lien vers ce fichier que vous pouvez partager sur des sites tiers.
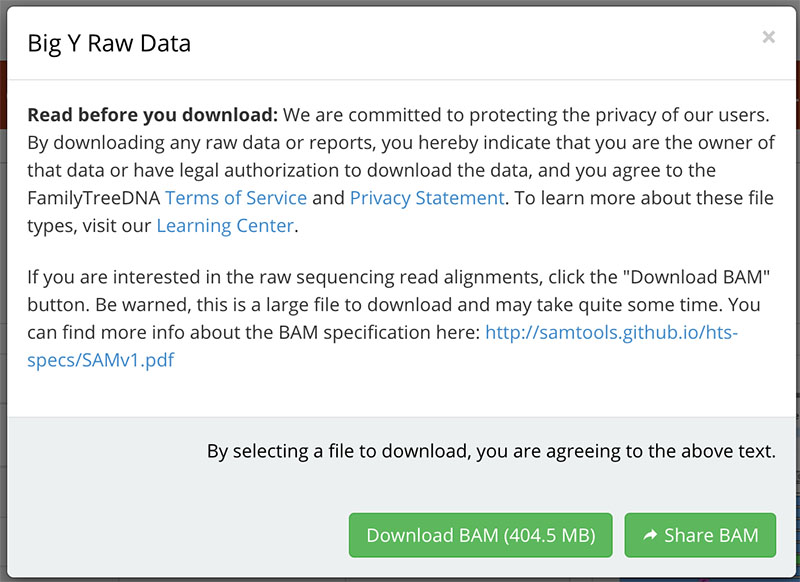
Une fois cette opération préalable réalisée, vous devez créer un compte sur YFull et pointer vers votre fichier BAM. YFull commence à analyser votre fichier pour vous confirmer s’il est exploitable, puis facture 49$ l’analyse.
L’objectif avec YFull est double :
- trouver des cousins génétiques qui matchent sur ma lignée paternelle, et identifier à quelle génération pourrait se trouver notre ancêtre paternel commun
- avoir davantage de précisions sur les SNPs qui sont propres à ma branche WOLF, visualiser à quel haplogroupe elle se rattache et contribuer à enrichir le Ytree
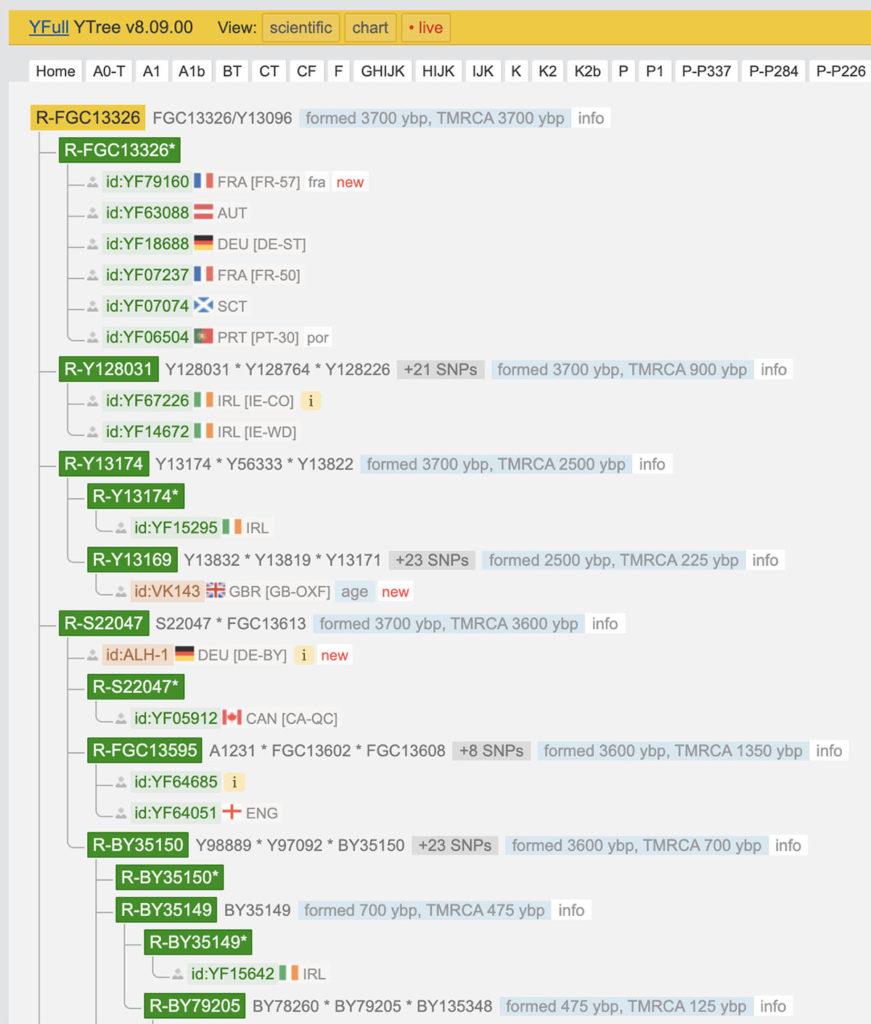
A l’heure où j’écris cet article, l’analyse de mon fichier BAM n’est pas encore complète. Pour l’instant YFull me rattache à l’haplogroupe R-FGC13326, formé il y a environ 3700 ans, en compagnie d’un Autrichien, d’un Allemand, d’un autre Français, d’un Ecossais et d’un Portugais (oui je sais on dirait le début d’une blague…)
Mais YFull a identifié un certain nombre de SNPs qui me sont propres, qui ne matchent avec aucun autre utilisateur, et qui a priori correspondent à des ancêtres plus récents. Dont le R-FGC34165 identifié aussi par Family Tree DNA, mais plusieurs autres que je pourrai étudier plus tard quand l’analyse YFull sera entièrement terminée.
Je rédigerai un article dédié à mes résultats sur YFull quand leur analyse sera terminée, et que je maîtriserai davantage toutes les subtilités de ce service…
SNP Tracker, un autre outil impressionnant
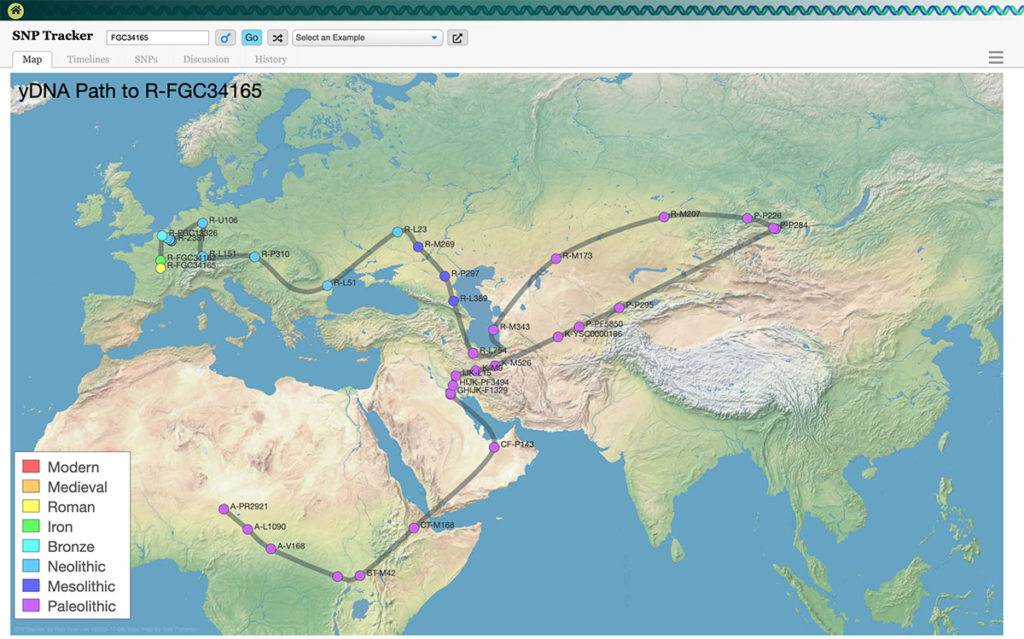
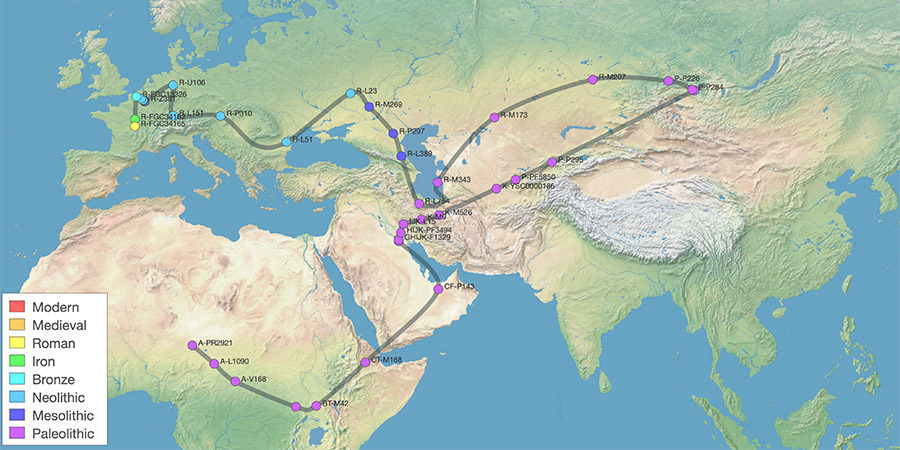
A partir du moment où on connait son haplogroupe le plus récent, on peut « ‘s’amuser » à tester des services qui proposent diverses analyses. Mon préféré est SNP Tracker, qui à partir de mon haplogroupe R-FGC34165 retrace (gratuitement) la migration de ma lignée paternelle depuis son berceau en Afrique au Paléolitihique jusqu’en France à l’Antiquité !
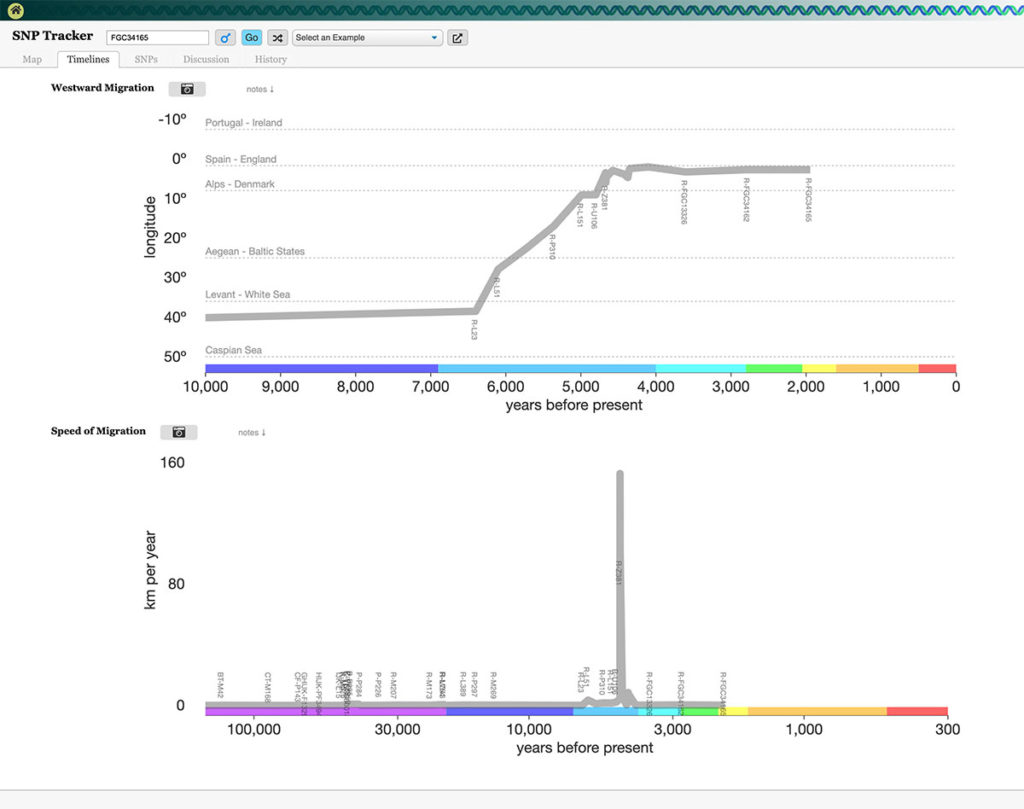
Les tableaux suivant aident à comprendre à quel rythme s’est déroulé cette migration, et relativiser la grande migration lors du Paléolithique qui a durée plusieurs dizaine de milliers d’année. Le rythme s’est surtout accéléré vers la fin Néolithique avant l’Âge de Bronze, quand ces ancêtres étaient déjà arrivés dans le nord de la France…
Un service que je regarderai d’encore plus près quand j’aurai un haplogroupe plus récent… mais qui fait bien le lien avec ce que j’ai appris des migrations humaines à la lecture de L’Odyssée des Gènes.
Prochaine étape : la création d’un projet de recherche ADN-Y spécifique aux Wolf du Grand Est
Sur Family Tree DNA, j’ai rejoint plusieurs projets qui regroupent des généalogistes autour des noms de famille ou des zones géographiques sur lesquels portent leur recherche. J’ai par exemple rejoint les groupes Woolf-Wolfe-Wolf, Germany-YDNA et R U106 (R1b-U106). Mais sans résultats probants pour l’instant, et avec des tableaux de comparaison beaucoup trop vastes et complexes pour trouver des réponses à mes recherches…
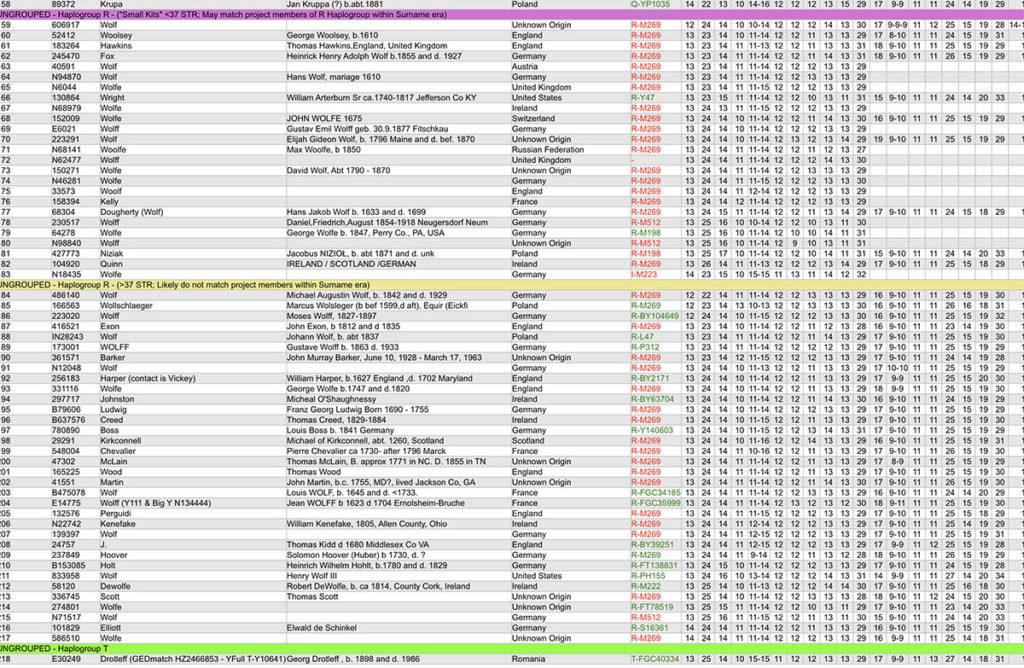
Si je veux avancer sur cette recherche Y, comprendre comment les différentes branches WOLF se raccrochent entre elles, et identifier d’où viennent les WOLF établis en Moselle après la Guerre de Trente Ans au-delà des limites des recherches généalogiques (Allemagne, Luxembourg, Suisse, Autriche, … ?), je n’ai pas le choix. Il faut que je lance mon propre projet Y, pour regrouper au sein d’une communauté les généalogistes qui travaillent sur ces mêmes problématiques, et contacter des descendants WOLF vivants qui seraient prêts à faire un test ADN-Y pour faire progresser nos connaissances communes. Affaire à suivre…

Bonjour,
Votre article est passionnant. J’ai également fait un test ADN-Y par curiosité. J’ai un arbre généalogique classique et mon AAGP Paternel est un enfant abandonné des hospices de Bordeaux. J’ai donc le nom de famille qu’il lui a été attribué. Ma question peut paraitre stupide, du fait que je débute tout juste dans la généalogie génétique, mais est-il possible qu’avec ce type d’analyse je puisse identifier le réel nom de famille de ma lignée paternelle ?
Je vous remercie par avance pour votre éventuelle réponse.
Bonjour « Carreau », acceptez-vous d’ échanger nos coordonnées, car je cherche un moyen de faire lentest Y.
Bonjour.
Oui c’est une bonne démarche de faire un test ADN-Y pour un ancêtre en lignée paternelle directe qui a été abandonné. Il vous faudra ensuite de la chance pour réussir à identifier de cette façon le nom de famille du père biologique de votre ancêtre, mais en théorie c’est tout à fait possible.
Tout dépend de la proximité génétique que vous avez avec vos matchs ADN-Y. S’ils sont suffisamment proches, c’est-à-dire au plus tard XVIe-XVIIe siècle quand sont apparus les noms de famille et les registres paroissiaux, vous pourrez avoir de bons indices sur le patronyme recherché. Mais si c’est au-delà vous ne pourrez rien en conclure, et vous devrez patienter pour avoir un match plus proche.
Quel est votre match le plus proche pour l’instant ?
Par exemple avec mon test ADN-Y, j’ai de nombreux matchs sur 25 marqueurs qui portent le patronyme « FINE », avec une distance génétique de 2. Ce qui confirme que j’ai forcément un ancêtre paternel commun avec eux, mais cela remonte à au moins 20-30 générations… Par contre ces 10 FINE matchent surement entre eux de façon beaucoup plus proche, et ils ont sans doute identifié leur ancêtre commun FINE grâce à ce test (et en comparant leurs arbres généalogiques).
Bonnes recherches !
[…] son fils Anthony « Tony ». Pour des raisons pratiques, c’est Tony à Brooklyn qui a fait le test Big Y de FamilyTreeDNA début […]
Bonjour,
Toutes mes félicitations pour cet article.
Avec le recul …Pensez vous que le Test BIG-Y du laboratoire Family Tree DNA (complété par YFull) permet de passer la barre de la 6eme génération ?
Cordialement
PL
Bonjour.
Merci pour votre message 🙂
C’est tout l’intérêt d’un test Y par rapport à un test autosomal, il permet en théorie de trouver des ancêtres à des générations beaucoup plus lointaines. Ce qui est compliqué ensuite c’est de réussir à les identifier…
Par exemple avec mon cousin Tony notre ancêtre paternel commun est à la 8ème génération, mais celà n’apparaissait pas dans le test autosomal, uniquement avec le test Y.
Bonjour,
Votre site est très intéressant.
J’ai moi-même des ancêtres en Moselle, réalisé mon test adn et celui de mon frère pour avoir l’haplogroupe paternel : R-P311.
Peut être sommes nous cousins ?
Etes vous sur GedMatch ou sur My Heritage ?
Merci pour votre retour.
Bien cordialement.